
最先端AI技術による高精度/高記述力の潜在空間学習と分子設計
大上 雅史
研究代表者
所属:東京科学大学情報理工学院 准教授
研究概要
本計画研究は、機械学習や化合物設計技術によって天然物から様々な情報を抽出し分子設計を主導するAI技術を開発します。これまでのAI技術では多くの天然物が該当するbRO5 (beyond Rule-of-Five) 空間への対応ができていませんでしたが、bRO5空間への手法の拡充や、ペプチドと合成小分子をつなぐ技術の開発に取り組みます。潜在空間からデザインされた化合物のインシリコスクリーニング評価や、他の計画班による実験的評価を踏まえ、AIによる潜在空間構築をさらに洗練させ、本領域が目指す潜在空間を応用した革新的な生物活性分子設計技術を実現します。
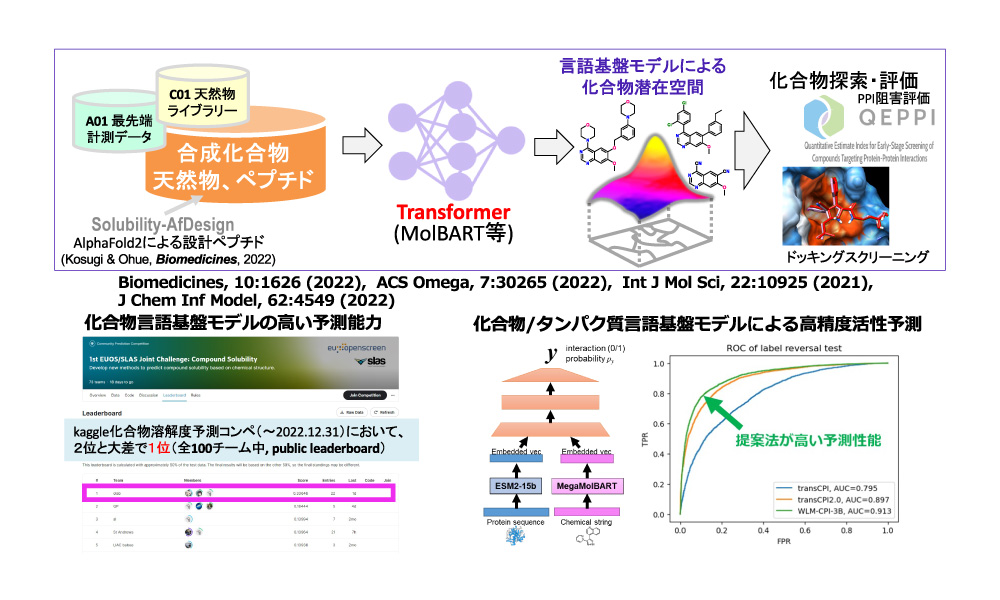
研究成果
- Kengkanna A, Ohue M. Enhancing property and activity prediction and interpretation using multiple molecular graph representations with MMGX. Communications Chemistry, 7: 74, 2024.
- Furui K, Ohue M. FastLomap: Faster Lead Optimization Mapper Algorithm for Large-Scale Relative Free Energy Perturbation. The Journal of Supercomputing, 80: 14417-14432, 2024.
- Ueki T, Ohue M. Antibody Complementarity-Determining Region Design using AlphaFold2 and DDG Predictor. The Journal of Supercomputing, 80: 11989-12002, 2024.
- Hu W, Ohue M. SpatialPPI: three-dimensional space protein-protein interaction prediction with AlphaFold Multimer. Computational and Structural Biotechnology Journal, 23: 1214-1225, 2024.
- 大上雅史. AlphaFoldによる高精度なタンパク質立体構造予測と創薬への応用. PHARM STAGE, 23(8): 24-28, 2023.
- Murakumo K, Yoshikawa N, Rikimaru K, Nakamura S, Furui K, Suzuki T, Yamasaki H, Nishigaya Y, Takagi Y, Ohue M. LLM Drug Discovery Challenge: A Contest as a Feasibility Study on the Utilization of Large Language Models in Medicinal Chemistry. In Proceedings of AI for Accelerated Materials Design (AI4Mat) NeurIPS 2023 Workshop, 2023.
- Ochiai T, Inukai T, Akiyama M, Furui K, Ohue M, Matsumori N, Inuki S, Uesugi M, Sunazuka T, Kikuchi K, Kakeya H, Sakakibara Y. Variational autoencoder-based chemical latent space for large molecular structures with 3D complexity. Communications Chemistry, 6: 249, 2023.
- Kosugi T, Ohue M. Design of cyclic peptides targeting protein–protein interactions using AlphaFold. International Journal of Molecular Sciences, 24(17): 13257, 2023.
- Ohue M, Kojima Y, Kosugi T. Generating potential protein-protein interaction inhibitor molecules based on physicochemical properties. Molecules, 28(15): 5652, 2023.
- Kengkanna A, Ohue M. Enhancing Model Learning and Interpretation Using Multiple Molecular Graph Representations for Compound Property and Activity Prediction. In Proceedings of The 20th IEEE International Conference on Computational Intelligence in Bioinformatics and Computational Biology (CIBCB 2023), 2023.
- Furui K, Ohue M. Faster Lead Optimization Mapper Algorithm for Large-Scale Relative Free Energy Perturbation. In Proceedings of The 29th International Conference on Parallel & Distributed Processing Techniques and Applications (PDPTA’23), 2023.
- Kosugi T, Ohue M. Solubility-aware protein binding peptide design using AlphaFold. Biomedicines, 10(7): 1626, 2022.
- Kosugi T, Ohue M. Quantitative estimate index for early-stage screening of compounds targeting protein-protein interactions. International Journal of Molecular Sciences, 22(20): 10925, 2021.
